仙桃学术 | 太火热了!4+铜死亡零代码生信SCI复现!今年国自然大热门主题!
继2019年自噬、2020年铁死亡、2021年细胞焦亡的纯生信研究风靡之后,2022年3月,美国哈佛大学和麻省理工学院布罗德研究所的TODD R. GOLUB团队在顶刊Science上提出并刷爆全科研网的“铜死亡(cuproptosis)”也不负众望,热度上升的速度堪比神十四,截止目前该领域已发表相关文章1000余篇,如何抓住新热点铜死亡变道超车?且看本期复现内容。
各位小伙伴大家好,本期给大家复现的是一篇2022年5月发表在4+的医学杂志Genes (Basel)上铜死亡的纯生信文章~
文章题目

文章背景
铜是生物过程中不可缺少的微量元素,研究表明,与健康对照者相比,肿瘤患者血清和肿瘤组织中的铜含量均明显升高。
2022年3月,TODD R. GOLUB团队发现了一种不同于已知的细胞死亡的新机制:铜依赖且受到调控的细胞死亡方式,即铜死亡,通过铜与三羧酸(TCA)的脂酰化成分直接结合,导致脂酰化蛋白的异常聚集和铁硫簇蛋白的丢失,从而导致蛋白毒性应激而导致细胞死亡。
体内铜平衡失调可能引发细胞毒性,细胞内铜水平的改变可能影响肿瘤的发展和进展。基于这一机制,铜离子载体(双硫仑、二硫代氨基甲酸酯、埃莱斯克洛莫等)和铜螯合剂(曲恩汀、四硫钼酸盐等)已被应用于抗癌治疗。
然而,铜死亡相关基因(CRGs)在肾透明细胞癌(ccRCC)中的临床影响尚不清楚。
在本研究中,作者探讨了CRGs在ccRCC中的差异表达、遗传改变、互作网络、临床预后、免疫相关性,为铜死亡调控在ccRCC中的治疗应用奠定了基础。
PS: science原文识别到了10个基因,其中7个正调控基因(FDX1、LIAS、LIPT1、DLD、DLAT、PDHA1、PDHB),3个负调控基因(MTF1、GLS、CDKN2A)。
文章思路
差异表达
- Figure 1:ccRCC患者中CRGs的表达和遗传改变
- Table S1:CRGs在不同数据集的差异表达结果
- Figure 5:GSE40435 、GSE53757和TCGA三个数据集的差异表达验证
功能聚类
- Figure 2:CRGs的功能富集(GO/KEGG)
交互网络
- Figure S1:CRGs的蛋白互作网络
- Figure 6:ccRCC中CRGs表达与免疫细胞浸润相关性
- Figure 7:CRGs与免疫检查点PD-1、PD-L1和TIM-3的相关性
临床意义
- Table S2:单因素/多因素Cox分析CRGs表达与ccRCC预后之间的关系
- Figure 3:CRGs在TCGA的ccRCC患者中的预后意义
- Figure 4:Nomogram的构建与验证
- Figure 8:CRGs在ccRCC不同病理分期及组织学分级中的表达差异
使用工具
仙桃学术工具 https://www.xiantao.love/
GENEMANIA数据库 http://genemania.org/
TIMER数据库 https://cistrome.shinyapps.io/timer/
复现步骤
Figure 1:ccRCC患者中CRGs的表达和遗传改变

(1)进入仙桃学术工具,左侧导航栏中选择表达差异(挑)中[云]非配对样本→选择肾透明细胞癌的数据集,分子输入铜死亡基因(CRGs):FDX1、LIAS、LIPT1、DLD、DLAT、PDHA1、PDHB、MTF1、GLS、CDKN2A,默认其它参数,点击确认即可得到CRGs在ccRCC及正常组织中的表达箱式图(Figure 1A)

(2)点击界面最下方数据下载链接,下载TCGA肾透明细胞癌的表达数据

提取铜死亡基因(CRGs):FDX1、LIAS、LIPT1、DLD、DLAT、PDHA1、PDHB、MTF1、GLS、CDKN2A的表达数据如下

进入仙桃学术工具( https://www.xiantao.love/),左侧导航栏中选择基础绘图中相关性热图-原始矩阵→上传上方数据,类型选择样式2和上半,默认其它参数,点击确认即可得到CRGs在ccRCC中的相关性热图(Figure 1B)

接着将显著正相关的DLD和DLAT表达数据提取如下
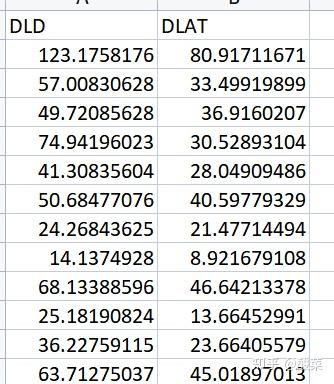
进入仙桃学术工具( https://www.xiantao.love/),左侧导航栏中选择基础绘图中相关性散点图→上传上方数据,样式选择样式3-两侧加分布图,默认其它参数,点击确认即可得到DLD和DLAT的相关性散点图(Figure 1B)

PS:原文Figure1C–1E中CRGs突变分析涉及到了R包,这里感兴趣突变分析的小伙伴可以参考阿琛老师的推文《想让文章拥有如此漂亮的患者突变可视化图?“maftools“包帮你解决》进行学习
这里和大家分享一个cBioPortal获取肾透明细胞癌中铜死亡基因突变概况图的方法:进入cBioPortal 数据库( http://www.cbioportal.org/),这里可选择样本量最多的肾透明细胞癌数据集,点击Query By Gene

默认相关参数,输入基因FDX1、LIAS、LIPT1、DLD、DLAT、PDHA1、PDHB、MTF1、GLS、CDKN2A,点击Submit Query

新的界面点击Download,即可下载ccRCC中CRGs的突变概况图

- Table S1:CRGs在不同数据集的差异表达结果

(1)进入仙桃学术工具( https://www.xiantao.love/),左侧导航栏中选择差异分析中[云]筛选分子→选择肾透明细胞癌数据,方法选择保留临床数据且去重重复样本,默认其它参数,点击确认

待分析完成后,点击Excel表格下载

即可得到TCGA中肾癌和正常组织的差异分析结果,提取CRGs在TCGA数据集中的差异分析的log2FoldChange和pvalue。

(2)进入仙桃学术工具( https://www.xiantao.love/),选择数据集检索,检索框输入GSE40435 数据集,点击下方GEO2R

设置分组信息并添加分组,点击Analyze

待分析完成后,点击download下载差异分析结果,提取CRGs在GSE40435 数据集中的差异分析的log2FoldChange和pvalue
同样方法可获取CRGs在GSE53757数据集中的差异分析的log2FoldChange和pvalue,最终将CRGs分别在TCGA、GSE40435 和GSE53757数据集中的log2FoldChange和pvalue汇总整理即为文中Table S1
- Figure 5:GSE40435 、GSE53757和TCGA三个数据集的差异表达验证

(1)进入仙桃学术工具( https://www.xiantao.love/),选择数据集检索,检索框输入GSE40435 数据集

点击数据平台GPL10558,弹出的界面点击Download full table下载探针信息

以及左下方数据下载,弹出的界面点击GSE40435_series_matrix.txt.gz下载

在GPL10558探针信息表中找到CDKN2A的探针

多个探针对应一个基因时,这里可以取均值,最终整理成如下数据格式

进入仙桃学术工具( https://www.xiantao.love/),左侧导航栏中选择基础绘图中分组比较图→上传上方数据,添加标题CDKN2A和纵坐标Expression,默认其它参数,点击确认即可得到GSE40435中CDKN2A的表达箱式图

同样操作可得到DLAT、FDX1、LIAS 在GSE40435和GSE53757中的箱式图
(2)借助仙桃学术工具按照前面Figure 1的步骤分别提取GSE40435、GSE53757和TCGA数据集中CDKN2A在肾透明细胞癌和正常组织中的表达值,并计算其mean值和SD值
进入Review Manager 软件,点击File→创建New→选择Intervention review→点击Next

选择Full review,点击Finish

选择Studies and references→点击Add Study,输入GSE40435,点击Finish

同样步骤添加GSE53757、TCGA,结果如下

点击Data and analyses→选择Add Comparison→Name栏输入CDKN2A,点击Finish


点击Add outcome→弹出界面选择Continuous,点击Next

后续弹出的对话框,默认相关参数(即原文中的随机效应模型),点击Next到最后或者直接点击Finish即可




点击Data and analyses中的CDKN2A,右键选择Add Study Data,

弹出的对话框选择TCGA、GSE40435和GSE53757,点击Finish

输入TCGA、GSE105437和GSE12470数据集中CDKN2A在正常组织和肾透明细胞癌中表达的mean值和SD值如下图所示

点击森林图标,即可弹出森林图

同样的方法也可获取DLAT、FDX1、LIAS 在TCGA、GSE105437和GSE12470数据集的森林图(PS:单基因多数据集验证时,除了常规表格、箱式图之外,这种森林图也是一个不错的呈现方式)
- Figure 2:CRGs的功能富集(GO/KEGG)

(1)进入仙桃学术工具,点击左侧导航栏中的功能聚类(圈)→GO/KEGG富集分析,分子列表输入CRGs,富集分析选择全部GO项目,点击确认

保存结果为GO并下载excel结果

点击左侧导航栏中的功能聚类(圈)→GO/KEGG可视化,选择分析好的项目GO,类型可选择柱状图,输入显示的富集条目,点击确认保存即可得到GO富集分析柱状图

同样操作可获取KEGG富集分析柱状图
- Figure S1:CRGs的蛋白互作网络

(1)进入GENEMANIA数据库( http://genemania.org/),左上角选择物种人,检索框中输入铜死亡相关基因(CRGs),点击检索按钮


即可得到CRGs的互作网络,点击左下角配色按钮可以对基因进一步标记颜色

PS:GENEMANIA数据库是由加拿大学者开发,最开始的数据库相关文章(PMID: 20576703)于2010年7月发表在Nucleic Acids Research杂志,是一个极简风格的基因功能预测与联系网站,GeneMANIA从GEO、BioGRID、IRefIndex和I2D以及生物体特有的功能基因组学数据集中收集了数以亿计的数据集和数以亿计的相互作用,目前支持9种生物(拟南芥、秀丽隐杆线虫、斑马鱼、果蝇、大肠杆菌、人、小家鼠、褐家鼠和酿酒酵母),通过搜索公开生物数据集来寻找相关的基因,包括蛋白-蛋白,蛋白-DNA 和遗传相互作用、通路、生理生化反应、基因和蛋白表达、蛋白结构域及表型筛选。
- Figure 6:ccRCC中CRGs与免疫细胞浸润相关性

进入TIMER ( https://cistrome.shinyapps.io/timer/)数据库,导航栏中选择Gene,Gene Symbol输入CDKN2A,Cancer Types中输入COAD,Immune Infiltrates默认B cell,CD8+ T cell,CD4+ T cell,macrophage,neutrophil ,dendritic cell ,点击Submit,即可得到文中Figure 6A

同样操作,Gene Symbol分别输入DLAT、FDX1、LIAS,即可的得到DLAT、FDX1、LIAS与免疫细胞浸润的相关性,即Figure 6B-6D
- Figure 7:CRGs与免疫检查点的相关性

进入仙桃学术工具,点击左侧导航栏中的交互网络(联)→分子相关性分析→[云]散点图,选择TCGA-KIRC的TPM格式数据集,输入分子CDKN2A和PDCD1,默认其它参数,点击确认,即可得到CDKN2A和PDCD1的相关性散点图

同样操作,基因A分别输入DLAT和FDX1,基因B分别输入PDCD1、CD274和HAVCR2,最终得到铜死亡基因CDKN2A、DLAT、FDX1和免疫检查点PDCD1、CD274、HAVCR2的相关性散点图
- Table S2:单因素/多因素Cox分析CRGs表达与ccRCC预后之间的关系

进入仙桃学术工具,点击左侧导航栏中的临床意义(靠)→预后分析→[云] 单|多因素Cox回归,选择TCGA-KIRC的TPM格式数据集,输入CRGs,类型选择OS(也可以选择DSS、PFI,下载对应的数据结果进行展示和后续分析)默认其它参数,点击确认

Word三线表下载即可得到单因素/多因素Cox分析CRGs表达与ccRCC预后表,同时下载RiskScore.xlsx备用

- Figure 3:CRGs在TCGA的ccRCC患者中的预后意义

(1)将前面Cox分析下载的RiskScore.xlsx和以及Figure 1 中得到的CRGs表达矩阵整合为如下数据格式(因原始数据处理方式的差异等,当前分析结果与原文稍有出入当前COX结果显示FDX1、DLAT是其独立预后因素,对于此大家不必拘泥于结果,掌握方法即可)

进入仙桃学术工具,点击左侧导航栏中的临床意义(靠)→预后分析→风险因子图,上传上方整理好的数据,默认其它参数,点击确认,即可得到FDX1和DLAT构建的针对OS结局的风险因子图


(2)进入仙桃学术工具,点击左侧导航栏中的基础绘图→生存曲线-二分类/数值/单组,上传下方数据,默认其它参数,点击确认,即可得到FDX1和DLAT构建的风险模型的生存曲线


进入仙桃学术工具,点击左侧导航栏中的基础绘图→生存曲线-二分类/数值/单组,上传下方数据,默认其它参数,点击确认,即可得到FDX1的生存曲线


同样操作可得到DLAT的生存曲线
(3)进入仙桃学术工具,点击左侧导航栏中的基础绘图→时间依赖ROC,上传下方数据,默认其它参数,点击确认,即可得到FDX1和DLAT构建的风险模型的时间依赖ROC曲线


同样将单因素/多因素Cox分析的结局变量换为DSS/PFI,下载对应的Cox结果重复上述步骤也可得到对应的风险因子图、生存曲线、ROC曲线
- Figure 4:Nomogram的构建与验证

(1)进入仙桃学术工具,点击左侧导航栏中的临床意义(靠)→预后分析→[云] 单|多因素Cox回归,选择TCGA-KIRC的TPM格式数据集,输入变量并设置分组信息,类型选择OS/DSS/PFI,默认其它参数,点击确认

点击Word三线表下载即可得到文中Figure 4A各临床变量及铜死亡独立预后基因的单因素/多因素Cox分析表

(2)进入仙桃学术工具,点击左侧导航栏中的临床意义(靠)→预后分析→[云]预后列线图(Nomogram),选择TCGA-KIRC的TPM格式数据集,输入变量并设置分组信息,类型选择OS/DSS/PFI,设置时间点,默认其它参数,点击确认,即可得到预后模型的列线图

(3)进入仙桃学术工具,点击左侧导航栏中的临床意义(靠)→预后分析→[云]预后Calibration分析,选择TCGA-KIRC的TPM格式数据集,输入Nomogram中的变量参数信息,类型选择Nomogram对应的OS/DSS/PFI,设置对应的时间点,默认其它参数,点击确认


待分析完成后,点击左侧导航栏中的临床意义(靠)→预后分析→[云]预后Calibration可视化,勾选已分析好的Calibration项目,点击确认,即可得到预后模型Nomogram的Calibration曲线

同样将Nomogram和Calibration分析的结局变量换为DSS/PFI,重复上述步骤也可得到对应的DSS/PFI的Nomogram和Calibration曲线
- Figure 8:CRGs在ccRCC不同病理分期及组织学分级中的表达

进入仙桃学术工具,点击左侧导航栏中的临床意义(靠)→[云]临床相关性,选择TCGA-KIRC的TPM格式数据集,输入临床变量分期并设置分组,分子输入基因FDX1,默认其它参数,点击确认,即可得到FDX1在ccRCC不同病理分期的表达箱式图

同样设置其它临床变量及分组,输入其它铜死亡基因,重复上述步骤也可得到对应的表达箱式图
整个流程走下来,是不是有种似曾相识的感觉?
没错,作为细胞死亡的新晋成员铜死亡,相比自噬、铁死亡、细胞焦亡而言,从数据内容上看,铜死亡只是换了一个基因集而已,所以自噬、铁死亡、细胞焦亡等研究的思路也可移花接木到铁死亡当中,比如铜死亡相关的单基因研究、铜死亡相关基因构建疾病预后signature的研究、基于铜死亡基因集对疾病分型的研究、铜死亡基因集的泛癌研究等等,套用到自己研究的疾病当中,鼠标点点点几篇SCI是不是就有了?
好啦,以上就是本次铜死亡生信文献复现分享的全部内容啦,愿屏幕前的你学有所获,下期再见,886
作者:灰灰
本文首发于“ 解螺旋”微信公众号
转载请注明:解螺旋·临床医生科研成长平台

文章被以下专栏收录


