GWAS(2) 在Linux服务器上安装plink
plink是一个免费、开源的全基因组关联分析(GWAS)工具集,旨在以计算高效的方式执行一系列基本的大规模分析。
下面介绍如何在Linux服务器上安装plink。
1. 进入plink 1.9官网,选择对应版本
官网链接:https://www.cog-genomics.org/plink/1.9/
鼠标放置上面,右键->复制链接:

2. 下载安装包并解压
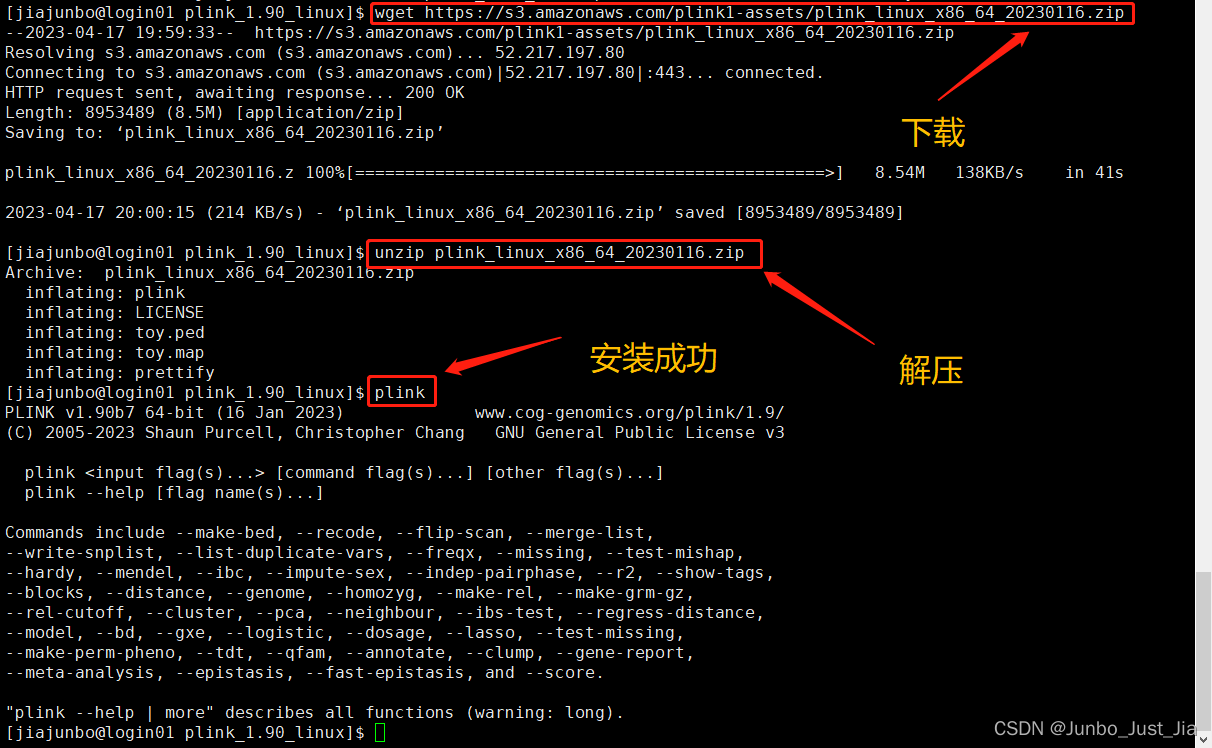
3. 配置路径
为方便后面执行plink,在.bashrc中写入plink的安装路径
首先,对于普通用户(非root用户),进入home目录,并打开.bashrc文件。
![]()
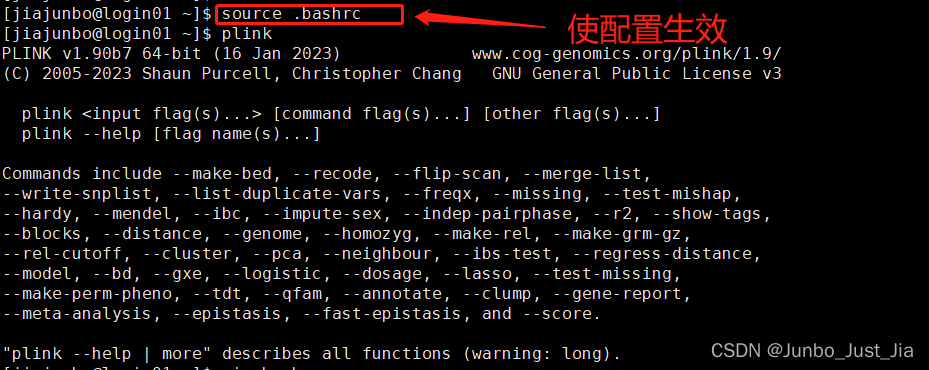
在bashrc文件后面写入plink的安装路径:

然后,保存退出, 使配置生效
4. 参考文献
【1】linux上安装plink
作者:贾思特
日期:2023-4-17





















 2687
2687










 暂无认证
暂无认证


















2301_79976768: 下载失败,链接被拒
No verão390: 请问出现debug提示该怎么处理?
CSDN-Ada助手: 非常感谢用户分享的这篇GWAS(1)全基因组关联研究(Genome-Wide Association Studies, GWAS)汇总,对于对这个领域感兴趣的人来说,这篇博客无疑是一份珍贵的资料。恭喜用户不断创作,希望用户能够继续分享更多有价值的内容,同时也建议用户在下一篇博客中加入更多详细的案例分析,这样读者更容易理解和学习。 CSDN 正在通过评论红包奖励优秀博客,请看红包流:https://bbs.csdn.net/?type=4&header=0&utm_source=csdn_ai_ada_blog_reply3,我们会奖励持续创作和学习的博主,请看:https://bbs.csdn.net/forums/csdnnews?typeId=116148&utm_source=csdn_ai_ada_blog_reply3
CSDN-Ada助手: 非常感谢你的分享,这篇博客对于了解LCWGS非常有帮助。恭喜你已经写了四篇博客,这是非常不容易的。希望你能够继续坚持创作,不断深入探究相关主题,也期待你能够分享更多的经验和见解。加油! CSDN 会根据你创作的前四篇博客的质量,给予优秀的博主博客红包奖励。请关注 https://bbs.csdn.net/forums/csdnnews?typeId=116148&utm_source=csdn_ai_ada_blog_reply4 看奖励名单。
CSDN-Ada助手: 非常感谢您的分享,这篇博客很有用!让我们学习如何在Linux服务器上安装plink,这将有助于我们更好地进行基因组关联分析。除了安装plink之外,您还可以学习如何在Linux中使用其他基因组关联分析工具,例如GCTA、BOLT-LMM等。希望您能继续分享更多关于基因组分析的知识,让我们一起学习! 如何写出更高质量的博客,请看该博主的分享:https://blog.csdn.net/lmy_520/article/details/128686434?utm_source=csdn_ai_ada_blog_reply2